Foram encontradas 910 questões.
Em um laboratório de pesquisa, uma amostra pura de uma substância foi utilizada para a construção de uma curva de absorção e, depois, foi submetida a uma diluição seriada. Os gráficos que representam, respectivamente, a curva de absorção da substância pura e a absorbância versus a concentração na diluição seriada estão na opção
Provas
Em uma placa de microtitulação, utilizou-se 5 μL de uma amostra de anticorpo para preparar uma diluição seriada até a obtenção da diluição de 1/512. Para isso, se utilizou 5 μL de tampão, previamente adicionado em cada poço da placa. Após homogeneização da amostra no primeiro poço, foi transferido 5μL da mistura para o poço 2 e, assim, sucessivamente. O poço que contêm a concentração de 1/128 é o
Provas
Tecnologia do DNA é um termo que descreve as técnicas coletivas para a obtenção, a amplificação e a manipulação de fragmentos de DNA específicos. O desenvolvimento dessa tecnologia revolucionou o estudo da biologia, abrindo muitas áreas de pesquisa para a investigação molecular. Quando é necessária a inserção de um gene em uma molécula DNA, é necessário que haja um corte nessa fita, e a maior parte dos cortes é realizada com a utilização de enzimas de restrição bacterianas. A enzima EcoRI (Escherichia coli) realiza cortes em zigue-zague apenas entre os nucleotídios G e A em cada filamento do DNA. A figura abaixo demonstra a ação da EcoRI.
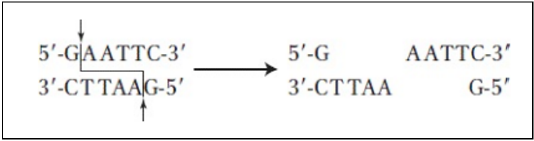
A Enzima EcoRI deixa as extremidades do filamento do DNA
Provas
O estudo do conteúdo da informação de todo o material genético de um organismos é denominado bioinformática. Dentro da bioinformática, é possível ter acesso ao inventário de todos os polipeptídios codificados pelo genoma desse mesmo organismo. Esse inventário é denominado
Provas
Um biomédico, em seu projeto de pesquisa, obteve o clone de um gene de interesse. A próxima meta é entender a função do gene para o organismo. Para isso, entre as metodologias que deverão ser empregadas, haverá o sequenciamento do DNA. Assim, o biomédico decide utilizar a técnica de sequenciamento de Sanger ou sequenciamento didesóxi por ser a mais conhecida. A seguir estão descritas, de forma aleatória, as etapas do sequenciamento de Sanger.
1 Começará a síntese do filamento de DNA complementar pela polimerase, iniciando a partir do primer marcado.
2 Enfileira-se os diversos fragmentos sintetizados, todos com o mesmo ponto de início e diferentes pontos de parada, do menor para o maior, com o didesoxinucleotídeo no final de cada fragmento. 3 Desnaturam-se os dois filamentos do DNA alvo.
4 A ação da polimerase é interrompida em qualquer ponto no qual o didesoxinucleotídio trifosfato for incorporado na cadeia de DNA em crescimento, no lugar do desoxinucleotídio trifosfato normal.
5 Cria-se um primer marcado radioativamente para a síntese de DNA que hibridizará, exatamente, em um local no segmento de DNA clonado.
6 Sabendo onde é o início da síntese do DNA e qual didesoxinucleotídeo finaliza cada fragmento de diferentes comprimentos, tem-se o sequenciamento total do DNA alvo.
7 Adiciona-se um “coquetel” especial de DNA polimerase, desoxinucleotídios trifosfato normais (dATP, dCTP, dGTP e dTTP), uma pequena quantidade de um didesoxinucleotídio das quatro bases (ddATP, ddCTP, ddGTP e ddTTP) e os primers.
Para realizar a técnica de sequenciamento corretamente, o biomédico deverá seguir a seguinte ordem de etapas:
Provas
Na biologia molecular, o método mais utilizado para a detecção de uma molécula linear de DNA dentro de uma mistura é o blotting. Nessa técnica, a mistura de moléculas é colocada em um poço formado em um gel de agarose que é submetido à eletroforese para separar as moléculas de DNA na mistura. Sobre o blotting e os processos associados a ele, considere as afirmativas abaixo.
I Após a eletroforese, as bandas podem ser cortadas do gel. O DNA genômico é digerido por enzimas de restrição e se usa uma sonda para identificar um fragmento nessa mistura. Essa técnica é denominada Northern blotting.
II Na eletroforese, os fragmentos de DNA são separados em classes de tamanhos distintos e formam bandas no gel. As bandas podem ser visualizadas por meio da coloração do DNA com prata, que causa a fluorescência do DNA na luz ultravioleta.
III Na eletroforese em gel de agarose, o gel contendo a mistura é posicionado em uma caixa com eletrodos nas extremidades, de modo que os poços estejam no polo negativo e o DNA migre até o polo positivo.
IV A velocidade de migração das moléculas de DNA, no gel da eletroforese, é inversamente proporcional ao seu tamanho, já que a agarose atua como uma peneira onde pequenas moléculas se movimentam mais fácil e rapidamente do que fragmentos maiores.
Das afirmativas, estão corretas
Provas
Considere a descrição da técnica abaixo.
|
“Todo o DNA de um genoma é quebrado em segmentos do tamanho ideal para ser inserido num vetor de clonagem, e se insere cada segmento em uma cópia diferente do vetor, criando, uma coleção de moléculas de DNA recombinante que, se consideradas em conjunto, representam o genoma inteiro. Em seguida, se transforma ou se infecta essas moléculas de DNA em células receptoras bacterianas em separado, nas quais elas serão amplificadas. Esse processo gera uma coleção resultante de bactérias ou bacteriófagos que contêm todo o DNA recombinante”. |
A coleção de DNA gerada, a partir da técnica descrita, é denominada de
Provas
Muitos cânceres humanos resultam de mutações em um gene normal as quais podem levar a um crescimento descontrolado de determinado tecido, conhecido como tumor. Os genes que causam câncer, quando mutados, são denominados oncogenes. A identificação de oncogenes clonados em biblioteca genômica é um processo conhecido como clonagem posicional, e sua estratégia é utilizar a posição genética para isolar o gene a ser estudado. Sobre a clonagem posicional, considere as afirmativas abaixo.
I Para iniciar a clonagem posicional, os pesquisadores precisam mapear, primeiramente, o gene responsável por uma característica em particular.
II Mesmo quando há marcadores localizados em cada lado do gene de interesse, não significa necessariamente que são os melhores para o processo.
III Para mapear o gene de interesse, os pesquisadores podem testar a sua ligação com marcadores de localização conhecida, como o RFLP e SNP.
IV Quando se localiza a “vizinhança” cromossômica do gene de interesse, já se identifica diretamente o gene procurado.
Das afirmativas, estão corretas
Provas
A replicação do DNA ocorre na forquilha de replicação, local onde a dupla-hélice está desenrolando, e os dois filamentos do DNA estão se separando. O processo de replicação do DNA prossegue, continuamente, na direção da forquilha de replicação em deselicoidização no filamento contínuo, e vários componentes participam desse processo na forquilha. Sobre o processo de replicação do DNA, observe o esquema abaixo.
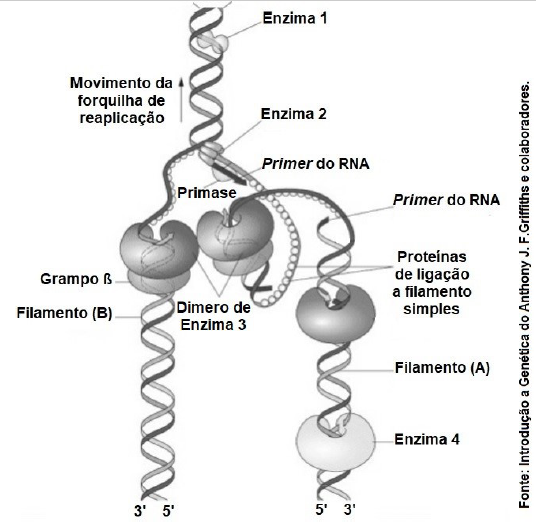
Na figura, a enzima 1 e o filamento B representam, respectivamente,
Provas
Os processos de transferência gênica em bactérias exigem que uma bactéria receptora receba um gene ou alelo de outra bactéria denominada doadora. A figura abaixo representa os mecanismos de recombinação gênica em bactérias, representados pelas letras A, B e C.
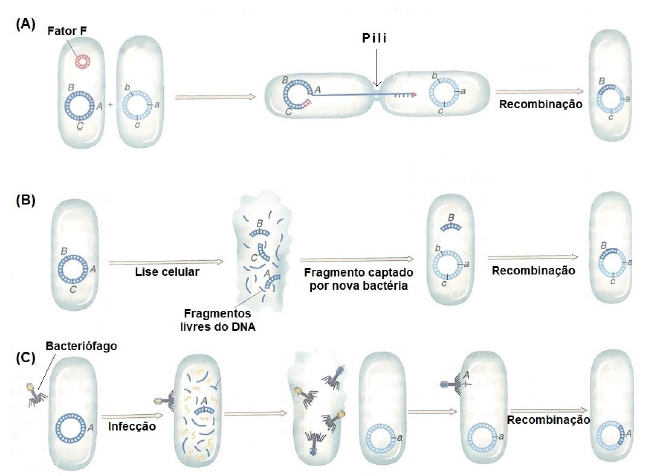
Fonte: Introdução a Genética do Anthony J . F. Griffiths e olaboradores .
A observação das etapas dos mecanismos de recombinação, explicitados na figura, permite evidenciar que ocorre, em
Provas
Caderno Container